Continuamos con la segunda parte hablando sobre los complementos que presenta el QGIS relacionados con temas de Biodiversidad. Tal como lo mencionamos en la anterior entrada, ahora trataremos sobre el complemento QSDM (QGIS Species Distribution Model).

QSDM Plugin
Básicamente el plugin incorpora modelos estadísticos para realizar el modelado de distribución de especies con QGIS, teniendo desde sus inicios el objetivo de ejecutar modelos MAXENT dentro de QGIS, pero el creador indica que su ambicioso plan es permitir contar con otras técnicas de modelado, tales como "RandomForests" y LogisticRegression. Para quienes han tenido la oportunidad de trabajar con MAXENT, se habrán dado cuenta que el principal requerimiento es, contar con la misma extensión y dimensiones de todos las coberturas de tipo ambiental de entrada, lo cual a veces es un poco dificultoso.
Para adelantarme en la descripción, con la herramienta "Unify Environmental Layers" presente en QSDM, podremos unificar nuestras coberturas de tipo ambiental a una resolución común y guardarlas como un archivo .asc de ESRI; esto gracias al excelente script de Yury Ryabov.
Otras de las herramientas disponibles con QSDM son:
- Calculate Niche Overlap Statistics: Permite calcular el grado de solapamiento o superposición del nicho utilizando la estadística de Schoeners D y la de Warren’s I basado en las distancias Hellinger para todos las coberturas de entrada. Los valores varían de 0 a 1, lo que representa respectivamente no superposición y una distribución idéntica.
- Range Shift: Muestra la diferencia entre dos capas de predicción de entrada. Por ejemplo, para las condiciones actuales y condiciones futuras.
- Create Species Richness grid: Crea un nuevo raster que contiene riqueza de especies y endemismo como capas de ocurrencia de entrada.
- Data Transformations: Hace transformaciones rápidas de capas raster de entrada.
- Modelado de distribución de especies: Tal como lo venimos indicando, se cuenta con la posibilidad de trabajar con el MAXENT (Máxima Entropía).
Configurando el Plugin
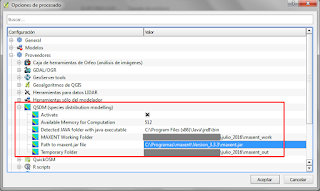
Lo primero que debemos asegurarnos es que tengamos instalado JAVA; del mismo modo debemos contar con la versión más reciente del Maxent y conocer la ubicación del archivo ejecutable (Maxent.jar) y también indicar nuestras carpetas de trabajo y las de salida. Todo ello debemos hacerlo dentro de las opciones de nuestra caja de herramientas de proceso.
Fig. 1: Configurando el Plugin QSDM para trabajar con MAXENT
Datos de Entrada para el MAXENT
Fig. 2: Sitio de descarga de los datos del WorldClim
Ejecutando el Modelo MAXENT
Ahora que tenemos los datos de entrada, para fines demostrativos vamos a trabajar con cinco variables: Altitud, bio1, bio5, bio6 y bio12, para conocer la descripción de las variables bioclimáticas, consultar aquí.
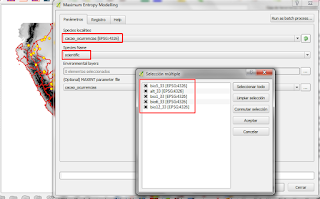
El paso siguiente será crear las condiciones para que el modelo Maxent pueda trabajar, por lo tanto, activamos la herramienta "Maximun Entropy Modelling" desde nuestro panel de procesos dentro del plugin. Luego debemos indicarle nuestro archivo de ocurrencias, asimismo nuestro campo que identifica a la especie y también debemos seleccionar las variables ambientales de entrada. Luego lo hacemos correr.
Fig. 3: Manejo de los archivos para trabajarlos con Maxent
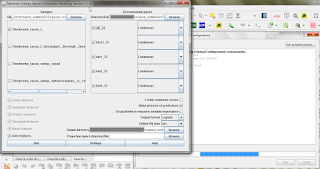
Cuando se está ejecutando la herramienta, podemos notar que está convirtiendo los archivos que estaban en formato GeoTiff hacia el formato *.asc; todos ellos se van almacenando dentro de la carpeta definida previamente como "maxent_out". Ahora si podemos ejecutar la otra herramienta "Maximun Entropy Modelling (Manual Configuration)", en donde de manera similar al anterior indicamos el vector con las ocurrencias, el campo de la especie y ahora le indicamos que las variables ambientales con la extensión adecuada se ubican en otro directorio.
Fig. 4: Ajustando los valores de acuerdo a los requerimientos del Maxent.
Al correr esta aplicación nos abrirá el entorno del Maxent, en donde ya se encuentra seleccionado la ruta tanto de la tabla con la especie en estudio y las variables ambientales en el formato que Maxent lo reconoce( *.asc); asimismo, podemos verificar que la carpeta de resultados será aquella que indicamos anteriormente como "maxent_work".
Fig. 5: Entorno del Maxent listo para ejecutarse.
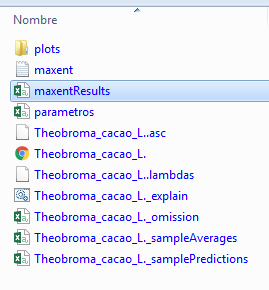
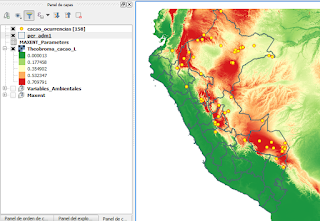
Al finalizar podremos apreciar todos los resultados que normalmente nos proporciona si lo trabajamos de manera independiente, pero ahora también se carga en nuestro QGIS el raster con la distribución de probabilidades.
Fig. 6: Lista de archivos como resultado del modelado.
Para efectos de visualización se ajustaron los colores de nuestro resultado obtenido.
Fig. 7: Resultado final obtenido mostrado en el QGIS.
En general el Maxent permite modelar la distribución geográfica de las especies, utilizando como datos sólo los sitios de presencia (en este caso se trabajó con datos de presencia de la especie Theobroma Cacao) y las variables bioclimáticas asociadas a cada uno de esos puntos de presencia. Para modelar las distribuciones se basa en el principio de Máxima Entropía. Para entender mejor nuestros resultados obtenidos, recomiendo revisar principalmente las referencias 5 y 6, en ellos se profundiza el tema de una manera didáctica. Bueno por mi parte espero haber contribuido a despertar un interés sobre este tema y que experimenten con el plugin.
Referencias:
- https://conservationecology.wordpress.com/qgis-plugins-and-scripts/qsdm/
- https://conservationecology.wordpress.com/2014/05/11/macroecology-for-qgis-the-new-qsdm-plugin/
- https://github.com/Martin-Jung/QSDM
- http://www.cs.princeton.edu/~schapire/maxent/
- https://www.cs.princeton.edu/~schapire/maxent/tutorial/tutorial-in-spanish.doc
- http://www.mncn.csic.es/docs/repositorio//es_ES//Blog/Documentos_blog/apuntes-sig-modelacion.pdf







6 comentarios:
Hola Carlos,
Muy buena esta entrada. Sin embargo, estoy tratando de seguir los pasos que describes pero no puedo ver dentro de las herramientas disponibles con QSDM la de Maxent y no se porque?
Muchas gracias por tu colaboración y seguimos en contacto.
Cordialmente,
Juan David
Hola Juan,
Para comentarte que luego de instalar el plugin, es necesario su configuración, en la entrada si te fijas en la Fig. 1, hay que establecer las rutas tanto de tu instalación de Java como del Maxent, luego recién te aparecerá la opción de Maxent.
Saludos,
HOLA BUENA TARDE, NO LOGRO INSTALAR el plugin QSDM, PODRIAR APOYAR PARA PODER REALIZARLO..
SALUDOS
Hola Mariana,
Te comento que cuando estuve intentando instalar en las nuevas versiones del QGIS tampoco tuve éxito, estoy tratando de descartar las causas, quizás sea la versión de Java. Si en algún momento logro resolverlo, escribiré un comentario al respecto.
saludos,
Hola, lamentablemente para la versión QGIS BONN sale este error; "Este complemento es incompatible con esta versión de QGIS Complemento diseñado para QGIS 2.0 - 2.99". Una pena.
Así parece Emilio, aunque igual tengo problemas en que me funcione en la 2.18. Esperemos que puedan actualizarlo para las nuevas versiones.
Publicar un comentario